Enzymfaktor im Dornröschenschlaf
Ein bislang unbekannter Mechanismus ermöglicht Antibiotikaresistenz in Bakterien
Forschende des Max-Planck-Instituts für terrestrische Mikrobiologie fanden einen bisher unbekannten Mechanismus der bakteriellen Transkriptionsregulation, der in Bakterien weit verbreitet zu sein scheint. Ihre Erkenntnisse könnten in Zukunft unter anderem dazu beitragen, Antibiotikaresistenzen zu bekämpfen.
Einleitung
In Ihrer Umgebung sind Bakterien häufig Veränderungen ausgesetzt. Um unter Stress oder wechselnden Lebensbedingungen zu überleben, müssen sie über physiologische Anpassungen schnell und adäquat reagieren. Dies geschieht meist durch eine spezifische Änderung der Genexpression. Daher ist die Transkriptionsregulation für Bakterien eines der wichtigsten Mittel, um sich an äußere Stressbedingungen anzupassen.
Alternative Sigma-Faktoren vermitteln Anpassungsreaktionen
Damit bakterielle Transkription stattfindet, muss zunächst eine Untereinheit, der so genannte Sigma-Faktor (σ-Faktor), an das RNA-Polymerase-Kernenzym binden und damit das vollständige und katalytisch aktive Holoenzym bilden. Jeder σ-Faktor erkennt andere Promotorelemente und bestimmt so die Ziele der Transkription. Bei externen Stressbedingungen wird der primäre σ-Faktor durch einen alternativen σ -Faktor ersetzt, der zur Transkription entsprechender Stress-Response-Gene führt. Unter den verschiedenen alternativen σ-Faktoren zählen extracytoplasmic function (ECF)- σ Faktoren zu den häufigsten. Sigma-Faktoren sind bekanntlich intrinsisch aktiv, was bedeutet, dass die Bakterienzelle sie in einem inaktiven Zustand halten muss, bis ihr Einsatz erforderlich ist.
Ein neuer Mechanismus der Transkriptionsregulierung
In Abwesenheit von externen Reizen wird der σ-Faktor meistens über Bindung an einen Anti-σ Faktor inaktiv gehalten. Im Falle eines spezifischen Stimulus wird der Anti-σ-Faktor inaktiviert und der σ- Faktor zur Interaktion mit der RNA-Polymerase freigesetzt.
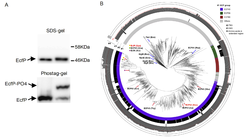
In Zusammenarbeit mit Forschern von SYNMIKRO in Marburg haben die Max-Planck-Forscher nun einen bisher unbekannten Mechanismus der Transkriptionsregulation aufgedeckt: er beruht auf inhärent inaktiven σ-Faktoren, die alleine nicht in der Lage sind, das RNA-Polymerase-Kernenzym zu binden. Erst durch Phosphorylierung an einem bestimmten Rest wird der σ-Faktor aktiviert und ist dazu in der Lage, die Expression bestimmter Gene zu steuern. Eine umfassende bioinformatische Analyse zeigte, dass diese Transkriptionsregulation durch σ-Phosphorylierung einen allgemeinen Mechanismus in Bakterien darstellt - ein neues Paradigma der Transkriptionsregulation.
"Eine besondere Eigenschaft dieses Mechanismus ist seine Modularität", erklärt Simon Ringgaard. "Unsere Entdeckungen zeigen, wie die Natur zwei unterschiedliche Regulationsmechanismen - Threoninkinase-Signalweg und Regulation der σ- Faktor-Aktivität - miteinander verschmolzen hat, die dann mit vereinten Kräften zur Anpassung befähigen.“
Der neue Sensor- und Signalweg regelt auch Antibiotikaresistenz
Ringgaards Modellorganismus ist zugleich ein wichtiges Anwendungsgebiet: das Bakterium Vibrio parahaemolyticus ist der weltweit häufigste Erreger der durch Meeresfrüchte verursachten Gastroenteritis beim Menschen. Die Max-Planck-Forscher indetifizierten ein ECF- σ- Faktor / Threonin-Kinase-Paar (genannt EcfP / PknT), das für die Vermittlung der bakteriellen Resistenz gegen Polymyxin bei V. parahaemolyticus verantwortlich ist. Die PknT-Kinase wird aktiviert, wenn die Zellen mit Polymyxin-Antibiotika behandelt werden. Aktiviertes PknT wiederum phosphoryliert und aktiviert EcfP, was zur Expression von Genen führt, welche die Antibiotikaresistenz hervorrufen.
Polymyxine sind eine Klasse von Antibiotika, die als Reservemittel zur Behandlung von Infektionen durch gram-negative Bakterien gelten. Da die Antibiotikaresistenz weltweit ein schwerwiegendes Problem für die öffentliche Gesundheit darstellt, ist es sehr wichtig zu verstehen, wie die Zellen die Resistenz regulieren, d.h. wie sie das externe Signal einer Antibiotikabehandlung verarbeiten und darauf reagieren. Die Identifizierung des Signalweges, der die Polymyxin-Antibiotikaresistenz bei V. parahaemolyticus reguliert, eröffnet neue Wege der Forschung zur Bekämpfung dieses und wahrscheinlich auch anderer menschlicher Krankheitserreger. Und letztlich liefert die Arbeit der Marburger Forscher grundlegende Erkenntnisse, die für das Verständnis der Regulation der Genexpression und der zellulären Anpassung im gesamten Bakterienreich wichtig sind.













